Ernst-Jan Eggers1,2, Ate van der Burgt1, Sjaak AW van Heusden2, Michiel E. de Vries@ 1, Richard GF Visser©2, Christian WB Bachem©2и & Pim Lindhout1
Ang genetic gain sa patatas gibabagan sa heterozygous tetraploid genome sa kultibado nga patatas. Ang pagbag-o sa patatas ngadto sa usa ka diploid inbred-line nga nakabase sa F1-hybrid nga tanum naghatag usa ka maayong ruta padulong sa dugang nga nakuha sa genetic. Ang pagpaila sa usa ka dominanteng S-locus inhibitor (Sli) nga gene ngadto sa diploid potato germplasm nagtugot sa episyente nga pagmugna sa mga liso nga na-fertilize sa kaugalingon ug sa ingon ang pagpalambo sa mga inbred nga linya sa patatas. Diyutay ra ang nahibal-an bahin sa istruktura ug gimbuhaton sa Sli locus. Dinhi among gihulagway ang pagmapa sa Sli sa 12.6 kb interval sa chromosome 12 gamit ang recombinant screen approach. Usa sa duha ka kandidato nga mga gene nga anaa niini nga agwat nagpakita sa usa ka talagsaon nga han-ay nga anaa lamang sa kaugalingon nga mga linya. Gihubit namon ang usa ka vector sa ekspresyon nga nagbag-o nga dili magkauyon sa kaugalingon mga genotype ngadto sa self-compatible ug usa ka CRISPR-Cas9 vector nga nag-convert sa SC genotypes ngadto sa SI. Ang Sli gene nag-encode sa usa ka F-box nga protina nga espesipikong gipahayag sa pollen gikan sa mga tanum nga nahiuyon sa kaugalingon. Ang 533 bp nga pagsal-ot sa promotor sa kana nga gene nagdala ngadto sa usa ka pag-uswag sa mutation sa function, nga nakabuntog sa pagsalikway sa selfpollen.
Ang patatas mao ang labing importante nga non-grain food crop sa kalibutan. Bisan pa, samtang ang ubang mga tanum nga pagkaon sama sa mais, bugas, ug trigo nagpakita sa usa ka genetic yield nga nakuha nga 1% matag tuig.1, gamay ra ang nakuha sa genetic sa patatas2. Sa pagkakaron, kadaghanan sa komersiyal nga gipatubo nga patatas nga mga kultivar nakuha gikan sa mga krus tali sa heterozygous autotetraploid nga mga ginikanan. Niini nga sistema sa pagpasanay, gatusan ka libo nga mga seedling ang namugna ug gi-screen sa matag breeding generation aron mailhan kadtong talagsaon nga mga indibidwal nga adunay madawat nga mga kinaiya alang sa daghang mga kinaiya nga naglainlain sa mga kaliwat. Tungod kay adunay mga kalim-an nga mga kinaiya nga may kalabutan sa bili sa usa ka komersyal nga patatas nga cultivar, ang kahigayunan sa paghiusa sa labing maayo nga mga alleles nga nagkontrol niini nga mga kinaiya gamit ang naandan nga pagpasanay sa patatas gamay ra. Dugang pa, ang gitumong nga pagpaila sa bag-ong mga kinaiya ngadto sa mga elite cultivars samtang ang pagmintinar sa genetic integrity pinaagi sa backcrossing schemes imposible nga walay homozygous nga linya sa ginikanan. Aron mabuntog kini nga mga problema, daghang mga grupo ang nagsugod sa inbred-line-based nga diploid nga mga programa sa pagpasanay sa patatas2-5. Niini nga mga programa, ang genetic gains makab-ot pinaagi sa incremental improvements sa parental lines pinaagi sa padayon nga pagpili batok sa deleterious alleles atol sa inbreeding ug pinaagi sa stacking beneficial alleles sa inbred lines pinaagi sa backcrossing schemes.6. Ang mga inbred nga linya sa ginikanan dayon gitabok aron makahimo og heterotic F1-hybrid nga mga anak.
Sa kadaghanan sa mga diploid nga patatas nga genotype, ang inbreeding limitado kaayo sa usa ka gametophytic self-incompatibility (GSI) nga sistema nga kontrolado sa multi-allelic S-locus. Kini nga S-locus nag-encode sa estilo nga nagpahayag sa S-RNases nga nagpugong sa pagtubo sa tubo sa kaugalingon nga pollen sa estilo, nga nagpugong sa pag-abono sa kaugalingon7. Atol sa cross-pollination, ang pollen-expressed S-locus F-box proteins (SLF) makaila sa S-RNases ug target kini sa proteasomal degradation pathway, nga magtugot sa pollen tube nga motubo paingon sa mga ovaries diin mahitabo ang fertilization.8. Ang matag S-allele nag-encode sa usa ka S-RNase ug daghang mga SLF nga adunay lainlaing mga espesipiko, nga magkauban makaila sa tanan nga S-RNase gawas sa S-RNase nga naa sa parehas nga allele.9.
Bisan tuod ang kadaghanan sa mga linya sa diploid nga patatas kay self-incompatible (SI), ang self-compatible nga diploid nga mga linya sa patatas anaa ug mahimong magamit sa pagpaila sa pagkaangay sa kaugalingon ngadto sa diploid potato breeding nga mga programa10-12. Si Hosaka ug Hanneman nagmapa sa usa ka dominanteng tigpugong sa S-locus (Sli) gene gikan sa a Solanum chacoense accession sa distal nga tumoy sa chromosome 12 ug gigamit kini sa pagmugna og mga inbred nga linya sa patatas13'14. Base sa ilang mga resulta, gisugyot kana ni Hosaka ug Hanneman sli usa ka gene nga gipahayag sa pollen nga adunay sporophytic nga aksyon ug kana nga homozygosity alang sa sli makamatay kay homozygous SliSli wala ang mga genotype sa F8 nga populasyon sa S. chacoense. Gigamit namon ang usa niini nga S. chacoense (DS) -nakuha nga inbred nga mga linya aron ipaila ang pagkaangay sa kaugalingon sa S. tuberosum mga background. Dinhi, gihulagway namon ang pag-ila sa hinungdan nga gene sa pagkaangay sa kaugalingon aron makakuha dugang nga panabut sa biology sa pagkaangay sa kaugalingon sa diploid nga patatas.
Mga sangputanan ug panaghisgutan
Sa usa ka F2 populasyon nga nakuha gikan sa usa ka krus tali sa sli donor (gitudlo nga DS) ug usa ka diploid S. tuberosum (D2) among naobserbahan ang usa ka kasarangan nga epekto sa QTL alang sa self-berry nga gibutang sa chromosome 2, apan ang sunod nga recombinant screening wala magmalampuson. Namatikdan namon nga daghang mga populasyon sa F2 ang nagpakita sa grabe nga pagkaliko sa palibot sa taas nga bukton sa chromosome 12, nga ang homozygosity alang sa non-DS haplotype hingpit nga wala.
Base sa kini nga skewness ug ang pagmapa sa sli sa chromosome 12, among gi-hypothesize kana sli gipahayag nga gametophytically, nga nagpasabot nga sa usa ka self-pollination sa usa ka tanom heterozygous alang sa sli (Sli/sli), pollen lamang ang adunay dominanteng sli Ang allele makaapil sa self-fertilization. Aron sulayan kini nga pangagpas, mitabok kami sa usa ka lig-on ug labi ka tabunok sa kaugalingon nga linya (16HP1-66) ngadto sa usa ka kusgan nga linya nga dili magkatugma sa kaugalingon (D16), ang tibuuk nga genome nga gisunod ang duha, ug gisusi ang sangputanan nga populasyon sa F1 (17SC11, n = 251, Fig. 1a, b). Tungod kay kini nga populasyon sa F1 kay polymorphic alang sa daghang mga loci, among naobserbahan ang usa ka halapad nga mga phenotypes, lakip ang mga adunay kalabutan sa pagkamabungahon. Busa, gipatuman namo ang usa ka estrikto ug higpit nga phenotyping protocol nga naglakip sa berry ug seed set gikan sa cross ug self-pollinations ingon man ang visualization sa pollen tube nga pagtubo sa mga estilo aron malikayan ang mga isyu sa sterility nga makalibog sa compatibility phenotype. Ang mga tanom nga nagbutang ug labaw sa usa ka self-berry gikonsiderar nga SC, samtang ang mga tanom nga wala magbutang ug self-berries human sa labing menos 10 ka self-pollinations, nagpakita sa self-pollen tube growth arrest sa estilo, ug nagbutang ug cross-berries human sa pollination nga may bulked. pollen giisip nga SI. Ingon usa ka sangputanan, usa ka hinungdanon nga bahin sa populasyon ang wala iapil sa mga pag-analisa sa genetic tungod kay ang mga kinahanglanon aron dili mahibal-an nga masusi ang compatibility phenotype wala matuman. Bisan pa, ang kahimtang sa pagkaangay sa kadaghanan sa populasyon nga 17SC11 progeny mahimong masusi ug kini gipakita nga gilain alang sa pagkaangay sa kaugalingon (Supplementary Data 1). Ingon nga ang pagkaangay sa kaugalingon naggikan sa 16HP1-66, gigamit namon ang tibuuk nga mga han-ay sa genome niini nga genotype sa pagdesinyo sa mga marka sa KASP nga nagpunting sa mga SNP sa mga chromosome 2 ug 12 nga heterozygous sa 16HP1-66 apan homozygous sa D16, nga makapaarang sa pagmapa sa sli sa maternal meiosis. Nagtukod kami usa ka genetic nga mapa, nagpahigayon sa pag-analisar sa QTL, ug nakit-an ang usa ka hinungdanon kaayo nga QTL (LOD = 75.72) sa taas nga bukton sa chromosome 12 (Fig. 1b), nagpamatuod sa mga resulta ni Hosaka ug Hanneman.
Aron makumpirma ang QTL sa usa ka lahi nga genetic background, among gitabok ang usa ka labi ka tabunok nga genotype nga nakuha gikan sa Solynta breeding program nga adunay SI genotype D14 ug gisusi ang sangputanan nga populasyon sa F1 (17SC25, Supplementary Data 1). Taliwala sa 32 ka mga indibidwal sa populasyon 17SC25, wala kami nakit-an nga mga indibidwal nga SI. Aron makamugna og segregating nga populasyon, gipili namo ang labing tabunok nga genotype ug gitabok kini ngadto sa duha ka SI genotypes nga among giila sa populasyon nga 17SC11, nga miresulta sa mga populasyon nga 18SC11 ug 18SC12 (Supplementary Data 1 ug Supplementary Fig. 1). Sama sa gipaabot, ang pag-analisa sa mga populasyon 18SC11 ug 18SC12 nagpakita nga ang duha ka populasyon naglain alang sa kaugalingon nga pagkaangay. Gisumite namo ang inahan (17SC25-8) alang sa tibuok genome sequencing ug gigamit kini nga datos sa pagdesinyo sa bag-ong mga marka sa KASP gamit ang sama nga pamaagi sama sa gigamit alang sa populasyon nga 17SC11, apan niining panahona gipunting lamang ang chromosome 12. Ang sunod nga pagtuki sa QTL nagpamatuod sa QTL nga among nakit-an sa populasyon 17SC11 nga adunay LOD nga mga kantidad nga 33.14 ug 120.94 sa mga populasyon nga 18SC11 ug 18SC12, matag usa (Supplementary Fig. 2).
Aron mahibal-an kung sli sa tinuud gipahayag nga gametophytically, among gisusi ang usa ka populasyon sa F2 (19SC1, n = 160) nga nakuha gikan sa usa ka tabunok ug kusog nga 17SC11 nga indibidwal. Ang pagpamulak ug pagkamabungahon niini nga populasyon mikunhod kon itandi sa F1. Sa phenotypic analysis, sa 160 ka tanom, 81 ka tanom ang self-compatible, 78 ang gi-categorize nga not determined (ND) tungod sa dili maayo nga pagpamulak o dili maayo nga fertility ug usa ka tanom ang nakuhaan og self-incompatible (Supplementary Data 1). Gidisenyo namo ang mga marka sa KASP nga nagpunting sa mga SNP sa chromosome 12 nga homozygous alang sa alternatibong mga alel sa mga ginikanan nga 16HP1-66 ug D16. Sa tibuuk nga chromosome 12 nga mga ratios sa paglainlain nga labi nga nagtipas gikan sa gipaabut nga 1: 2: 1 nga pagbulag. Dugang pa, sa palibot sa selfcompatibility QTL, walay loci homozygous alang sa haplotype sa ginikanan D16 (Supplementary Fig. 3), nga nagpakita sa baylo nga usa ka 1: 1 segregation alang sa heterozygous D16 / 16HP1-66: homozygous 16HP1-66, nagsugyot nga ang pagwagtang sa kulang sa pollen sli hinungdan sa segregation distortion. Gisuportahan niini ang pangagpas nga ang pollen lamang ang nagdala sa dominanteng sli Ang allele moapil sa selffertilization. Dugang pa, gawas sa usa ka indibidwal, ang phenotyping kay konklusibo alang sa kalainan tali sa SI ug SC, nga nagpakita nga ang gigamit nga phenotyping protocol lig-on ug halos walay sayop.
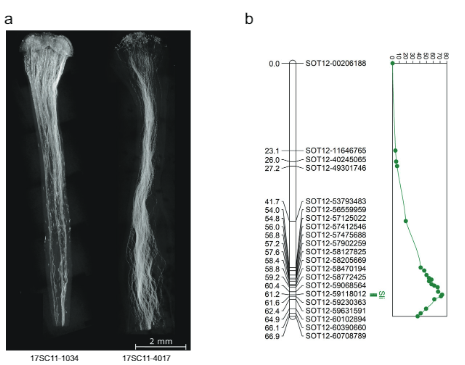
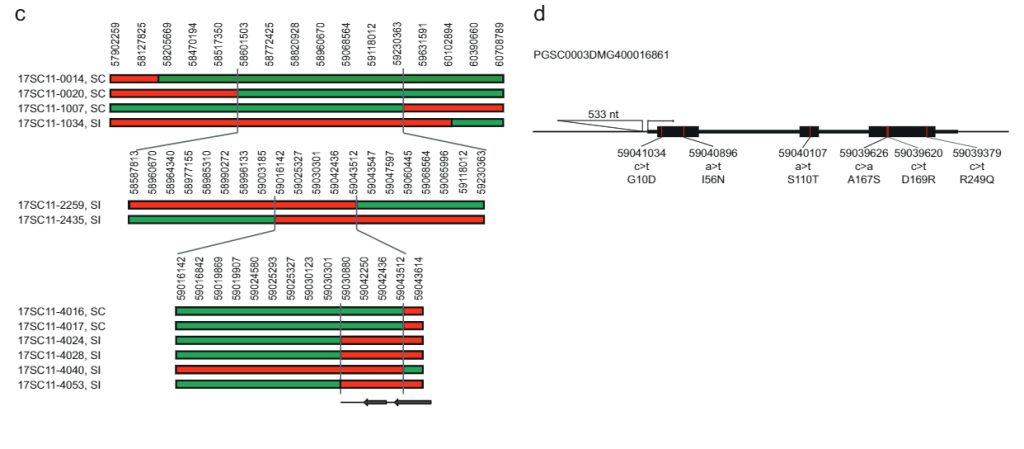
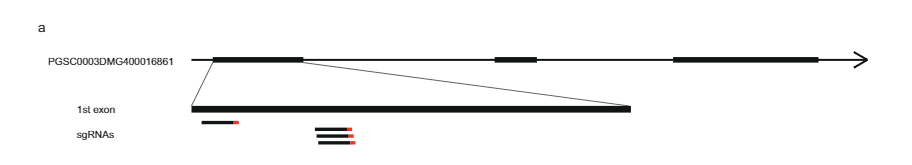
Samtang ang 628 KB SLI Ang agwat sa chromosome 12 nga nagdala sa Sli-allele gikan sa populasyon 17SC11 gikunhoran ngadto sa mas gamay nga nagsapaw-sapaw nga agwat sa 169 KB sa populasyon 18SC12, kini nga mga agwat dako pa kaayo aron mailhan ang Sli-gene. Busa, gitumong namo ang pagpakunhod sa S/i-containing interval pinaagi sa recombinant screening approach. Aron mahibal-an ang mga tanum nga adunay recombination sa sli interval, gi-genotype namo ang 1374 17SC11 nga mga seedling nga adunay duha ka marka sa KASP sa proximal nga utlanan ug duha sa distal nga utlanan. Among giila ang 81 ka seedlings nga adunay recombination tali sa duha ka pinakagawas nga marker ug gipili ang para sa dugang nga maayong pagmapa. Aron makuha ang dili klaro nga mga phenotype, gipakaylap namon kini nga mga genotype ug gihimo ang phenotyping sa labing menos duha ka mga clone matag genotype. Gi-genotype namo ang 81 nga mga recombinant nga adunay daghang mga marker sa interval ug giila ang duha ka informative recombinants nga nagpamenos sa interval ngadto sa 27.37 KB nga adunay lima ka annotated genes (Supplementary Data 1).
Aron madugangan ang pagkunhod sa agwat, among gi-screen ang laing 10165 ka mga seedling gikan sa samang populasyon nga adunay upat ka mga marker sa palibot niini nga 27.37 KB nga agwat ug giila ang 12 ka recombinant. Kini dugang nga genotyped nga adunay 14 pa nga mga marker sa kini nga agwat ug among giila ang unom ka informative recombinants nga nagpakita sa tin-aw nga compatibility phenotypes. Duha ka recombinant nga adunay SC phenotype ug usa nga adunay SI phenotype nagpamatuod sa distal nga utlanan sa 27.37 KB interval, samtang ang tulo ka recombinants nga adunay SI phenotype naghubit sa usa ka bag-ong proximal nga utlanan nga nagpamenos sa interval ngadto lamang sa 12.6 kb nga adunay duha ka mga gene, PGSC0003DMG400016861 ug PGSC0003DMG400016860 ug XNUMX Fig. 1c).
Aron mahibal-an ang kandidato nga gene nga responsable sa selfcompatible phenotype, among gi-analisar ang pagkasunud-sunod nga pagkalainlain alang niining duha nga mga gene sa daghang mga tibuuk nga genome nga sunud-sunod nga mga linya sa patatas nga diploid (Supplementary Data 2). Pinaagi sa pagtandi sa kini nga pagkalainlain sa pagkasunod-sunod sa mga phenotypes sa SC / SI sa kini nga mga linya, nahibal-an namon ang tanan nga mga piho nga SC nga SNP ug INDELS (Supplementary Data 2). Sunod, among gipaila ang tanan nga dili parehas nga mga SNP ug gitino kung ang mga pagpuli sa amino acid sagad o talagsaon alang sa parehas nga mga protina sa Solanaceae. Ang kandidato nga gene PGSC0003DMG400016861 nagpakita ug unom ka SC-specific amino acid substitutions ug ilabina, usa ka 533 bp insertion nga nahimutang sa —108 bp gikan sa pagsugod nga codon, nga nagsugyot nga ang SC allele nag-usab sa ekspresyon kumpara sa SI allele. Pinasukad sa kini nga genetic nga mga pagtuon, among gi-hypothesis nga ang PGSC0003DMG400016861 mao ang sli gene
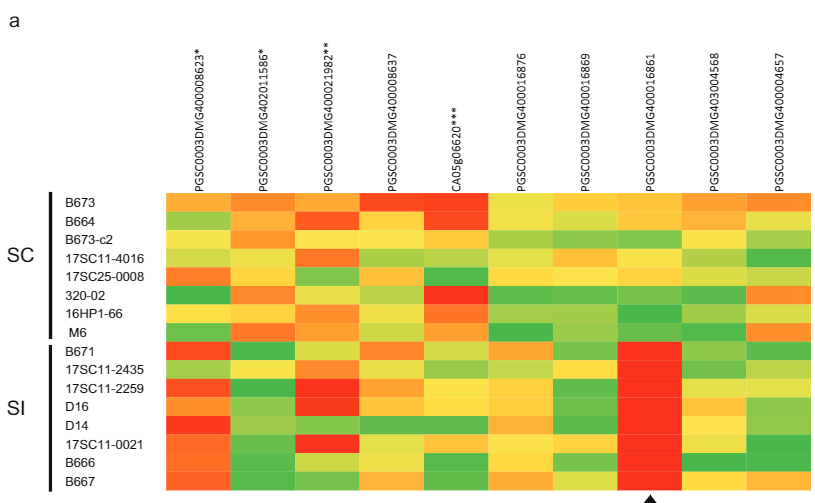
Aron mapamatud-an ang pangagpas nga ang Sli gipahayag sa pollen, among gipatubo ang pollen gikan sa 10 SI ug 10 SC nga mga genotype sa patatas sa vitro ug gikuha ang RNA alang sa pagsunud sa RNA. Gikan sa duha ka nahabilin nga mga kandidato nga gen, ang kandidato nga gene lamang nga PGSC0003DMG400016861 ang gipahayag, apan eksklusibo sa pollen gikan sa mga genotype sa SC (Fig. 2a). Dugang pa, sa mga tanum nga heterozygous alang sa putative nga kandidato nga Sli gene, ang Sli allele ra ang gipahayag. Makapainteres, ang ubang mga gene nga gipahayag sa pollen nga nahimutang duol sa Sli locus sa Chromosome 12 nagpakita sa parehas nga lebel sa ekspresyon sa mga tanum nga SC ug SI (Fig. 2a). Busa, nakahinapos kami nga ang PGSC0003DMG400016861 gene lamang ang espesipikong gipahayag sa mga tubo sa pollen sa mga tanum nga SC.
Aron imbestigahan ang gigikanan sa 533 bp insertion, among gihimo ang BLAST search sa 533 bp sequence sa NCBI. Makapainteres, ang mga han-ay nga susama kaayo sa Sli-specific insertion kay kasagaran sa sequenced S. tuberosum mga aksesyon (Fig. 2b). Dugang pa, ang pagsal-ot sa 533 bp adunay homology sa usa ka han-ay sa S. pennellii. Gamit ang sequence gikan sa S. pennellii ingon usa ka pangutana sa BLAST nakit-an namon ang parehas nga mga han-ay sa S. lycopersicum. Phylogenetic analysis sa mga han-ay sa S. tuberosum, S. pennellii ug S. lycopersicum mga grupo sa S. pennellii pagkasunodsunod uban sa S. lycopersicum ug usa S. tuberosum han-ay, nga nagsugyot nga kini adunay usa ka komon nga gigikanan (Supplementary Fig. 4a). Gipanghimatuud namon nga ang pagsulud nakuha gikan sa usa ka transposable nga elemento (TE). Naghimo kami og dot-plot graph gikan sa 533 bp sequence ug naobserbahan nga ang sequence adunay gamay nga inverted repeats (Supplementary Fig. 4b). Among gisumite ang 533 bp insertion sa BLAST batok sa plant MITE database, nga miresulta sa daghang hit gikan sa MITE family DTA_Sot42 sa S. tuberosum15, nga nagpakita nga ang 533 bp insertion sa promoter sa sli sa pagkatinuod naggikan sa usa ka TE (Supplementary Fig. 4c).
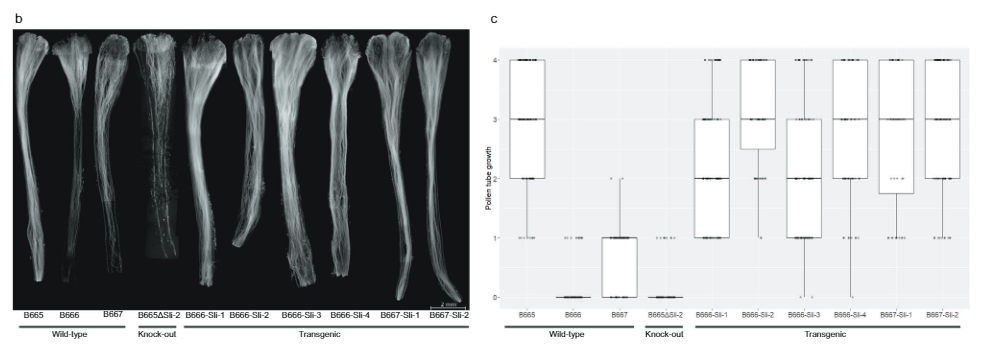
Aron dugang nga kumpirmahon nga ang PGSC0003DMG400016861 mao gyud sli, nagdesinyo kami og usa ka ekspresyon nga pagtukod nga adunay mga exon sa SC allele sa sli tali sa iyang lumad nga tigpasiugda ug terminator (Fig. 3a) sa vector pBINPLUS (pBINPLUS-Sli). Gigamit namo kini nga konstruksyon aron mabag-o ang duha ka SI genotypes gikan sa pagmapa sa populasyon 18SC12. Gi-phenotype namo ang duha ngadto sa unom ka clone gikan sa matag usa sa lima ka independenteng transgenics nga nakuha gikan sa SI genotype B666, ug tulo ka transgenics nga nakuha gikan sa SI genotype B667.
Ang mga clone gikan sa unom ka independyenteng transgenics dali nga nagbutang sa mga berry sa kaugalingon nga polinasyon (Supplementary Data 3). Dugang pa, ang fluorescence microscopy nagpakita nga ang pollen gikan sa sli Ang transgenic nga mga tanum motubo nga mas lawom ngadto sa kaugalingon nga mga estilo kay sa wala mausab nga mga kontrol (Fig. 3b, c). Naka-iskor kami sa pagtubo sa pollen tube sa 442 nga self-pollinations sa sli transgenics ug 179 ka self-pollinations sa untransformed controls sa 0-4 scale. Ang kadaghanan sa mga tubo sa pollen nakaabot sa mga obaryo sa kadaghanan sli transgenics, kon itandi sa gamay ra kaayong bahin sa mga kontrol, nga nagpakita nga ang PGSC0003DMG400016861 mao ang sli gene
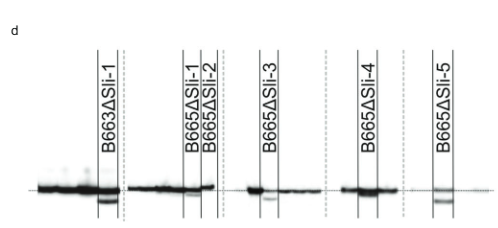
Sunod, gidesinyo namon ang usa ka CRISPR-Cas9 nga pagtukod nga nag-encode sa upat nga gRNA nga gipunting ang una nga exon sa PGSC0003DMG400016861 (pAGM: CRISPRASli, Fig. 3a). Gibag-o namo ang duha ka SC genotypes (B665 & B663) uban niini nga konstruksyon ug nakuha ang 149 ka nabag-o nga mga regenerant. Gisusi dayon namo ang gipunting nga exon gamit ang PAGE aron mahibal-an ang CRISPR-Cas9-induced INDELs. Ikasubo, ang pAGM:CRISPRASli vector adunay ubos nga kahusayan, unom lamang sa 149 nga mga regenerant ang nagpakita sa mga INDEL sa sli (Fig. 3d). Ang lima niini nga mga linya sa CRISPR-Cas9 heterozygous alang sa mga INDEL, apan usa ka linya, B665ASli-2, homozygous alang sa gamay nga INDEL. Samtang ang wala mabag-o nga B665 dali nga nagbutang sa kaugalingon nga mga berry ug nagpakita sa maayo nga pagtubo sa tubo sa kaugalingon pinaagi sa 105 nga naobserbahan nga mga istilo, ang B665ASli-2 wala magbutang mga berry sa kaugalingon nga polinasyon ug ang pollen dili makatubo pinaagi sa 78 nga naobserbahan nga mga istilo (Fig. 3b, c ug Supplementary Data 3), nga naghatag dugang nga ebidensya nga ang PGSC0003DMG400016861 mao gyud ang sli gene
Sa S-RNase-based gametophytic self-incompatibility system, ang self-fertilization gipugngan pinaagi sa pistil nga gipahayag nga S-RNases nga mosulod sa mga pollen tubes ug adunay cytotoxic effect sa self-pollen o bisan unsang pollen nga walay katugbang nga S-Locus F-box (SLF). ) protina. Ang cross-fertilization gipalihok pinaagi sa pollen-expressed SLF proteins nga makaila ug maka-detoxify sa dili-kaugalingon nga S-RNases. Ang matag S-allele nag-encode sa daghang mga SLF nga ang matag usa makaila sa lahi nga S-RNase, ug magkauban makaila sa kadaghanan sa mga S-RNase nga naa sa patatas gawas sa S-RNase nga gi-encode sa parehas nga S-allele. Ang Sli nag-encode sa usa ka F-box protein PP2-B10, nga naglangkob sa usa ka F-box domain nga nalambigit sa usa ka lectin domain. Ang mga domain sa lectin nahibal-an nga makig-uban sa mga carbohydrates, ug mahimo nga makig-uban sa mga glycosylated nga protina16. Dugang pa, ang S-RNases gipakita nga glycosylated17. Gipanghimatuud namon nga ang pagsal-ot sa 533 bp sa tigpasiugda sa SC allele sa Sli makapahimo sa ekspresyon sa pollen, diin ang Sli makahimo sa pagbugkos ug pag-detoxify sa kaugalingon nga S-RNases, nga mosangpot sa pagkawala sa self-pollen tube growth arrest ug sa ingon pagkaangay sa kaugalingon. Usa ka detalyado nga imbestigasyon sa kalihokan sa MITE sa mga patatas ni Laimbeer nakit-an nga 2% sa mga pagsulud sa MITE duol sa mga genic nga rehiyon adunay kalabotan sa mga pagbag-o sa ekspresyon sa gene.
Dugang pa, gikan sa 1935 nga gisulayan nga pagsal-ot sa hAT duol sa genic nga mga rehiyon, ang 13 miresulta sa upregulation sa kaubang gene, nga nagpakita nga ang giusab nga pollen-specific nga ekspresyon sa sli Mahimo nga tungod sa 533 bp nga pagsal-ot sa tigpasiugda niini18. Bisan pa, gikinahanglan ang dugang nga panukiduki aron mahibal-an ang kabalido niini nga hypothesis.
Kaniadto, si Clot et al migamit ug usa ka bulked segregant K-mer mapping approach aron mailhan ang 333 kb interval sa chromosome 12 diin ang Sli kinahanglang mahimutang.19. Dinhi, among gimapa ang Sli locus sa parehas nga rehiyon sa chromosome 12 sa usa ka F1 nga populasyon ug gigamit ang usa ka recombinant screening aron makunhuran ang agwat sa 12.6 KB nga adunay 2 nga mga gene. Ang pag-analisar sa ekspresyon nagpadayag nga ang SC allele sa usa niini nga mga gene espesipikong gipahayag sa pollen gikan sa mga genotype sa SC. Sa katapusan, gamit ang transgenic nga ekspresyon ug CRISPR-Cas9-induced knock-out, among gipakita nga ang PGSC0003DMG400016861 mao ang Sli. Samtang ang pagtuon ni Laimbeer nagpakita nga ang MITEs maka-upregulate sa mga proximate nga mga gene sa usa ka tissuespecific nga paagi, dugang nga panukiduki ang gikinahanglan aron pamatud-an nga ang presensya sa MITE sa Sli promoter mao ang hinungdan sa iyang pollen-specific nga ekspresyon.
Sa mga materyales nga gi-imbestigar niini nga pagtuon (Supplementary Data 4), dili namo makumpirma ang naunang mga taho sa lethality nga may kalabutan sa homozygosity para sa Sli, tungod kay nakit-an namon ang mga tanum nga F2 nga homozygous alang sa Sli nga nakahimo sa pagtakda sa mga berry (Supplementary Data 1)12>20. Dugang pa, ang mga han-ay sa genome sa inbred-line nga Solyntus, ingon man ang inbred-line nga M6, nagpakita nga kining duha ka mga linya homozygous alang sa Sli, nga nagpakita nga ang homozygosity alang sa Sli mismo dili makamatay, bisan kung posible pa nga usa ka makamatay. Ang allele nga genetically nalambigit sa Sli sa usa ka katigulangan gikuha pinaagi sa recombination niini nga mga genotypes21'22. Bisan pa, gikan sa mga datos nga nahimo sa kini nga pagtuon, dili naton maapil ang posibilidad nga ang paglainlain nga pagtuis nga naobserbahan sa populasyon sa F2 tungod sa usa ka lethal allele nga nalambigit sa hugna sa SI allele sa Sli. Sa pagkakaron, dili klaro kung ang Sli mismo direktang makaila ug maka-detox sa S-RNases. Dugang pa, dili klaro kung ang Sli nagresulta sa pagkaangay sa kaugalingon sa tanan nga S-locus genotypes. Posible nga ang pag-obra sa pipila ka S-aleles dili mapugngan sa Sli. Ang dugang nga panukiduki gikinahanglan aron masulbad kini nga pangutana.
Samtang ang pag-ila sa Sli dugang nga makahimo sa inbred-line-based hybrid breeding gamit ang diploid nga patatas, ang ubang mga babag nagpabilin. Una, ang labing hinungdanon, ang diploid nga patatas nag-antos sa inbreeding depression, nga mosangpot sa pagkunhod sa kusog ug pagkamabungahon sa inbreeding. Ang paghinlo sa makadaot nga mga alleles pinaagi sa padayon nga pag-abono sa kaugalingon sa mga linya sa diploid nga patatas usa ka episyente nga pamaagi aron makunhuran ang inbreeding depression ug miresulta na sa pagmugna sa medyo kusog ug tabunok nga mga inbred nga linya sa patatas.2'23-25. Ikaduha, ang donor sa Sli nga gigamit niini nga pagtuon, DS, nakuha gikan sa usa ka S. chacoense accession, nga posibleng mosangpot sa mga isyu sa linkage drag sa makadaut nga mga alleles gikan sa S. chacoense. Sa diploid breeding program sa Solynta, wala kitay makita nga mga isyu tungod sa makadaut nga mga alleles gikan sa S. chacoense. Dugang pa, ang usa ka bag-o nga pagtuon bahin sa pagkaangay sa kaugalingon nagpadayag nga ang mga k-mer nga piho sa SC naa na sa daghang mga kultivar nga tetraploid, nga naghatag usa ka ruta aron malikayan kini nga potensyal nga pagdugtong sa tibuuk pinaagi sa paggamit sa mga dihaploid nga nahimo gikan sa kini nga mga kultivar ingon mga Sli donor.19.
Pamaagi
Mga materyales sa tanum. Ang tanang gigamit nga materyales sa tanom gilista sa Supplementary Data 4
Mga kahimtang sa greenhouse. Ang tanan nga mga tanum gipatubo sa mga greenhouse nga gipainit kung ang temperatura nahulog sa ubos sa 14 ° C ug gipabugnaw pinaagi sa pag-abli sa mga bintana kung ang temperatura misaka labaw sa 19 ° C. Gidugangan sa artipisyal nga suga ang natural nga kahayag sa dihang ang intensity sa kahayag mius-os ubos sa 85 W/M2. Ang mga tanum gipatubo sa usa ka espesyal nga patatas nga substrate mix gikan sa Lentse Potgrond (Lentse Potgrond BV, Katwijk, Netherlands). Ang substrate mix nga gigamit kay gilangkuban gikan sa peatmixture para sa balanse nga tubig uptake, basic slow-release fertilizer, ug apog aron masiguro ang gikinahanglan nga pH level. Ang substrate mix giabono gamit ang 20:20:20 Nitrogen: Phosphorus: Potassium solution nga adunay electrical conductivity (EC) nga 1.5.
Pagtimbang-timbang sa pagkaangay sa kaugalingon. Ang mga bulak ug mga putot giihap kausa sa usa ka semana ug ang kalagsik gi-iskor kausa sa usa ka bulan sa timbangan gikan sa 1 hangtod 9 nga adunay 1 nga dili kaayo kusog nga tanum, ug ang 9 usa ka labi ka kusog nga tanum. Ang pollen gikan sa daghang mga bulak gikan sa usa ka tanum gikolekta sa usa ka Eppendorf tube ug gigamit dayon alang sa kaugalingon nga polinasyon sa parehas nga mga bulak nga adunay labing taas nga 10 ka bulak matag tanum matag semana. Ang mga tanom nga nagbutang ug labaw sa duha ka self-berries nga adunay dili mominus 35 ka liso kada self-berry giklasipikar nga self-compatible. Aron mahibal-an ang pagkamabungahon sa babaye, ang mga tanum gi-pollinated nga adunay bulked pollen gikan sa labing menos tulo nga wala’y kalabutan nga genotypes. Ang mga tanum nga wala magbutang sa kaugalingon nga mga berry pagkahuman sa labing menos 10 nga pag-pollinasyon sa kaugalingon, apan nagbutang ug labing menos usa ka bulk berry ug nagpakita nga tabunok nga pollen sa mikroskopikong pag-analisar sa mga istilo nga gi-pollinate sa kaugalingon giklasipikar nga dili magkauyon sa kaugalingon. Alang sa 40 ka genotypes gikan sa mga populasyon sa pagmapa diin ang datos sa berry ug binhi wala matino (17SC11: n = 14, 18SC11: n = 7, 18SC12: n = 19), ang phenotypical nga klasipikasyon gibase sa pagtubo sa tubo sa kaugalingon pinaagi sa mga estilo (namatikdan sa Supplementary Data 1).
Paghulagway sa estilo. Aron mahanduraw ang pagtubo sa pollen tube, ang mga pollinated nga estilo gikuha 24-48 ka oras pagkahuman sa polinasyon ug dayon gi-fix sa 3:1 nga ethanol:acetic acid sulod sa labing menos 24 ka oras. Ang mga estilo dayon gi-macerated sa 8M NaOH sulod sa 10 min sa 65 °C ug gihugasan kaduha sa deionized nga tubig. Ang mga estilo gibutang sa microscopy slides ug namansahan sa 2-5 min gamit ang 0.1% Aniline blue (Carl Roth GmbH) sa 0.1MK4P2O7 (pH = 7), dayon gi-squash sa glycerol gamit ang coverslip ug giobserbahan gamit ang Zeiss Axiolab fluorescence microscope gamit ang filter set 01 (BP 365/12, FT 395 ug LP 397). Ang tanan nga mga estilo giobserbahan ug gi-iskor gamit ang duha ka mga parameter: (1) pinakalawom nga pagsulod sa estilo, ingon nga gipahayag sa porsyento sa maximum penetration, (2) % sa pollen tubes nga nakaabot sa pinakalawom nga penetration. Dayon among gi-convert kini nga mga porsyento ngadto sa usa ka 0-4 nga sukdanan, diin ang mga estilo diin walay pollen tube nga nakaabot sa ovary nakakuha og score nga 0, mga estilo diin tali sa 0 ug 25% sa pollen tubes nakakuha og score nga 1, mga estilo diin tali sa 25 ug 50% sa pollen tubes nakaabot sa ovary nakakuha ug score nga 2, styles diin tali sa 50 ug 75% sa pollen tubes nakaabot sa ovary nakakuha ug score nga 3, ug mga styles diin labaw sa 75% sa pollen tubes nakaabot sa ovary nakuha. score nga 4.
Pagkuha sa litrato. Ang pinili nga mga estilo gilarawan gamit ang Zeiss Axiophot microscope nga adunay filter set 01, gamit ang Zeiss AxioCam ICc 5. Ang mga hulagway gihimo gamit ang Zeiss Zen 2.3 (blue edition) software package. Atol sa pag-angkon, ang mga setting gi-adjust aron mamenosan ang background. Gihulagway ang mga estilo gamit ang x5 nga tumong ug gitipigan isip TIFF files nga adunay resolusyon nga 2464 x 2056 pixels nga adunay 24-bit nga giladmon. Moabot sa walo ka separado nga mga hulagway ang gitigom gamit ang Panavue image assembler. Ang kalainan ug kahayag sa mga estilo nga gitigom gipasibo sa paghimo sa Fig. 1a ug 3c.
Pagkuha sa DNA. Para sa pagtuki sa KASP sa mga populasyon sa pagmapa, ang mga sample sa dahon gipadala ngadto sa VHLGenetics (Wageningen, The Netherlands) para sa DNA extraction gamit ang sbeadex™ kits (LGC Genomics GmbH, Berlin, Germany) sumala sa protocol nga gihatag sa manufacturer.
Pagtuki sa KASP. Ang competitive allele-specific PCR (KASP ™) analysis gihimo sa VHLGenetics (Wageningen, The Netherlands) gamit ang KASP assays nga gidisenyo nga espesipiko alang sa mga SNP nga naglain sa atong materyal. Ang mga pagsulay sa KASP gihimo sumala sa protocol nga gihatag sa tiggama (LGC Genomics GmbH, Berlin, Germany). Ang mga resulta gikan sa KASP assays makita gamit ang SNPviewer (anaa sa lgcgroup.com/products/genotyping-software/snpviewer) aron makumpirma ang husto nga segregation ug genotype nga pagtawag.
Pag-analisa sa sumpay. Ang mga haplotype sa kaugalingon nga katugbang nga babaye nga mga ginikanan gitukod pag-usab gikan sa datos sa genotype pinaagi sa pag-analisar sa mga rate sa recombination tali sa lainlaing mga SNP. Kini nga datos gigamit sa pag-convert sa mga tawag sa SNP ngadto sa usa ka "axb" nga format, diin ang "a" haplotype nalambigit sa self-compatible allele sa Sli, samtang ang "b" haplotype nalambigit sa usa ka self-incompatible allele sa Sli. Ang linkage nga mga mapa gihimo gamit ang Joinmap 4.126 uban ang tipo sa populasyon nga DH ug default nga mga setting.
Pagmapa sa QTL. Ang datos sa phenotype gi-convert ngadto sa numerical trait pinaagi sa pag-assign sa 1 sa matag self-compatible genotype, 0 sa matag self-incompatible genotype, ug * sa genotypes diin ang compatibility dili matino. Ang QTL mapping gihimo gamit ang interval mapping sa MapQTL27. Ang mga output sa MapQTL gigamit sa pagmugna og mga QTL plot gamit ang Mapchart 2.328.
Pagtuki sa bioinformatic. Aron mahibal-an ang husto nga mga modelo sa gene sa inisyal nga 27.37 kb interval, among gisusi ang duha ka separado nga anotasyon sa gene para sa DM4.04 nga reference genome, ang PGSC nga anotasyon, ug ang ITAG annotation. Tan-awa usab ang Hirsch et al.29. Aron makumpirma ang pagkahusto sa mga anotasyon, gihimo namon ang mga pagpangita sa BLASTp nga adunay gitagna nga mga han-ay sa protina gikan sa duha nga mga anotasyon. Pinaagi sa pagtandi sa labing maayo nga mga hit sa pagpangita sa BLASTp sa among pangutana, among nahibal-an kung ang tanan nga annotated nga mga exon ug mga domain sa gitagna nga han-ay sa protina gisuportahan sa parehas nga mga protina sa patatas ug uban pang mga species sa tanum. Dugang pa, magamit sa publiko ang RNA-seq nga mga librarya sa SPUD DB (anaa sa solanaceae.plantbiology.msu.edu/cgi-bin/gbrowse/potato/) ug NCBI genome data viewer (anaa sa ncbi.nlm.nih.gov/genome/gdv /browser/) gigamit aron mahibal-an kung ang mga putative exon adunay ebidensya sa ekspresyon. Sa tingub, kini nga duha ka mga pamaagi nagtugot kanamo sa pag-validate sa intron-exon nga mga istruktura sa mga modelo sa gene sa duha nga mga anotasyon, nga miresulta sa usa ka nahibal-an nga pagpili alang sa usa o daghang mga isoform sa mga modelo sa gene aron magrepresentar sa gene nga gipangutana. Pinasukad niini nga mga pamaagi, ang gene sa kandidato nga PGSC0003DMG400016862 giila nga lagmit partial ug gamay nga gipahayag ug gisalikway gikan sa dugang nga pag-analisar. Ang modelo sa gene nga Sotub12g029970 giisip nga husto, samtang ang PGSC nga katugbang niini nga PGSC0003DMG400016860 lagmit naputol. Tungod kay kini nahimutang sa kadaghanan sa gawas sa gitudlo nga agwat, ug wala'y kalabutan nga mga amino acid nga pagpuli sa taliwala sa mga tanum sa SC ug SI nga mahimong mailhan, kini nga gene gisalikway gikan sa dugang nga pag-analisar.
Pagtuki sa kalainan. Aron mahibal-an ang mga mutasyon sa 27.37 kb nga agwat nga espesipiko alang sa mga katugbang sa kaugalingon nga genotype ang tanan nga taas nga pagsalig sa SNPs (Supplementary Data 3) gitino nga (1) homozygous sa DS, 17SC100-18 ug 17SC100-2 (tungod kay ang tanan nga tulo homozygous alang sa ang SC allele sa Sli (Sli/Sli')'), (2) homozygous lainlain sa D16 (tungod kay ang D16 homozygous alang sa SI allele sa Sli (sli / sli)), ug (3) heterozygous sa 16HP1-66 ug 17SC25-8 (tungod kay ang duha heterozygous alang sa SC allele Sli (Sli) /sli)). Ang allelic sequence nakuha pinaagi sa de novo assembly gamit ang SPAdes version 3.11.130 sa 150 nt paired-end Illumina data sa nalista sa ibabaw nga mga tanom (sa gibana-bana nga 25-30X sequencing giladmon). Ang mga resulta nga contigs gipahiangay sa pakisayran sa DM (gamit ang minimap2 nga bersyon 2.1) ug gisala alang sa mga kasaligan nga pag-align sa 27 kb. Gikan niining mga aligned contigs, ang variation relative sa DM4.03 gi-quantify nga prangka (gamit ang subroutines mpileup ug tawag gikan sa bcftools, version 1.9) ug gilista sa Variant Call Format (VCF).
Pag-analisar sa pagbag-o sa amino acid. Gikan sa kini nga lista sa mga mutation nga espesipiko sa SC, ang tanan nga dili parehas nga mga SNP giila pinaagi sa pagsapaw sa gitudlo nga mga coding exon. Gilista ang mga pagbag-o sa amino acid nga may kalabotan sa pagkasunod-sunod sa DM o SI. Ang talagsaon nga mga pagbag-o sa amino acid giila pinaagi sa paghimo sa BLASTp nga pagpangita gamit ang pagkasunod-sunod sa protina ug paghimo sa daghang pagkasunod-sunod nga pag-align gamit ang top 100 BLASTp hits.
Pagkalainlain sa mga rehiyon sa promoter ug terminator. Ang promoter nga rehiyon gipili aron mahimong sunod-sunod nga upstream sa start codon hangtod sa coding sequence sa upstream gene nga adunay maximum nga 1500 nt. Ang dramatikong pagbag-o sa mga rehiyon sa tigpasiugda nakit-an sulod sa 27.37 kb nga agwat, diin ang labing katingad-an mao ang daghang dagkong mga pagtangtang ug pagsal-ot sa napulo ngadto sa gatusan ka mga nucleotide ang gitas-on. Ang tanan nga kalainan sa Sli interval, nga may kalabotan sa DM, nakuha, lakip ang sa promotor / upstream nga rehiyon ingon man ang terminator / downstream nga rehiyon.
Pagkuha sa pollen ug pagtubo. Ang pollen gikan sa mga genotype nga gilista sa Fig. 2a nakuha pinaagi sa pagkurog sa bukas nga mga bulak gamit ang electronic toothbrush ug pagkolekta sa pollen sa 1.5 ml nga Eppendorf tubes. Pagkahuman sa pagkuha, ang pollen gipauga pinaagi sa pagtipig sa bukas nga mga tubo sa Eppendorf nga adunay pollen sa usa ka kahon nga na-sealed sa hangin nga adunay silica gel sa 24 ka oras sa temperatura sa kwarto. Pagkahuman, ang pollen gitipigan sa -20 °C hangtod magamit pa.
Ang pollen gipatubo pinaagi sa pagsuspinde sa 2.5 mg nga uga nga pollen sa 5 ml nga likido nga medium (9% (w/v) sucrose, 50 mg/l Boric acid, 73.5 mg/l CaCly2H2O, 118 mg/l Ca (NO3)24H2O, 123 mg/l MgSO.4VH2O) sa 3.5 cm diyametro Petri pinggan gitakpan sa parafilm. Ang pollen gipasagdan nga moturok sa Petri dishes sulod sa 24 ka oras sa kangitngit sa usa ka nag-uyog nga incubator sa temperatura sa lawak ug nag-uyog sa 125 RPM. Ang liquid medium nga adunay sulod nga germinated pollen gi-pipetted pag-ayo ngadto sa 2 ml Eppendorf tubes gamit ang pipette tips nga giusab aron madugangan ang aperture size aron dili makadaot sa pollen tubes. Ang mga tubo sa Eppendorf dayon gi-centrifuge sa 600xg sulod sa 1 min ug ang medium gikuha pag-ayo pinaagi sa pipetting. Ang pellet ug pipila nga nahabilin nga medium dayon gi-frozen dayon sa liquid nitrogen, duha ka stainless steel beads (2 mm diameter) ang gidugang ug ang mga sample gigaling gamit ang TissueLyser II (Qiagen GmbH, Hilden, Germany) sa 20 Hz sa 1 min.
RNA extraction ug sequencing. Ang buffer RLT (Qiagen GmbH) gidugang sa gigaling nga mga sample sa pollen samtang gisiguro nga ang mga sample nagpabilin nga nagyelo. Ang RNA extraction gihimo dayon gamit ang RNeasy mini kit sumala sa protocol sa tiggama (Qiagen GmbH, Hilden, Germany). Ang 250-300 bp insert-size nga cDNA nga mga librarya gisunod-sunod isip 150nt paired-end reads, nga naghatag ug 30-42 million read-pares kada sample (Novogene, Cambridge, United Kingdom).
Ang ubang mga set sa datos sa RNA-seq. Aron makahimo og usa ka kinatibuk-ang ideya sa (tissue-specific) nga lebel sa ekspresyon, ang tanan nga gipares-katapusan nga sequenced RNA-seq data set nga gi-tag isip ORGANISMO "Sola-num tuberosum" Gi-download gikan sa publiko nga domain (NCBI-SRA, petsa 2018/17/13), nga adunay total nga 441 nga gipares nga fastq data set. Gikan niining 441 ka public data set, 3 ang namugna gikan sa style tissue (SRR7402817-SRR7402819) ug ang uban pa gikan sa lain-laing non-pollen tissues, developmental stages, ug accessions sa mga tanom.
Solyntus reference assembly. Para sa pag-analisar sa ekspresyon, ang bag-o lang nakuha nga draft assembly sa homozygous reference line nga Solyntus (bersyon 1.0, ma-download sa www.plantbreeding.wur.nl/Solyntus/) gigamit isip reference genome. Ang Solyntus kay usa ka homozygous nga barayti nga namugna isip kabahin sa breeding program sa Solynta21. Ang mga agwat sa pagmapa niini nga pagtuon nakuha gikan sa DM v4.03 genome assembly31 ngadto sa Solyntus 1.0 genome assembly pinaagi sa sukaranan nga mga pagpangita sa pagkaparehas (gamit ang BLASTn ug bedtools) nga mahimutang sa (Solyntus 1.0 genome assembly coordinates) 53532708-53954293 (Interval I, 421.6kb < —628.9kb), 53683239-53867377 (184.1kb) kb< — 168.7kb), 53731620-53763003 (Interval III, 31.4kb< —27.4kb) ug 53753977-53763003 (Interval IV, 9.0kb < —12.6 kb), matag usa. Sa taliwala sa mga bracket mao ang sunod-sunod nga mapping interval number [Solyntus 1.0 coordinates], gidak-on sa Solyntus-1.0, ug gidak-on sa DM-4.03/4.04, matag usa. Ang tanan nga mga agwat nahimutang sa chromosome ST4.03ch12_RaGOO (nahimong chromosome 12) ug wala’y usa ka gintang sa Solyntus 1.0 nga asembliya. Ang kalainan sa gidak-on sa agwat tungod sa daghang mga gaps (N's) sa katugbang nga han-ay sa DM ug daghang kalainan tali sa duha ka genome. Katugbang nga mga agwat sa DM genome (DM-4.03/4.04): Interval I: chr12:58601503-59230363, Interval II: chr12:58962004-59130723; Interval III: 59016142-59043512; Interval IV: chr12: 59030880-59043512.
Ang anotasyon sa gene sa Solyntus 1.0 nakuha gikan sa tulo ka lahi nga mga katalogo sa gene (patatas DM4.03, ITAG4.0 Tomato Genome Annotation Release sa Sep 6, 201932, ug Pepper-v. 1.5533), nga gimapa sa Solytus assembly pinaagi sa paggamit sa GeMoMa (v1.6.1). Gihimo kini aron mabayran ang mga pagkadili hingpit sa indibidwal nga mga katalogo sa gene ug mapadako ang atong kahibalo sa pagkaanaa sa posible nga mga gene ug/o gipahayag nga loci.
RNA-seq read-mapping ug transcript abundance quantifikasyon. Ang tanan nga 5 SC, 3 SI, ug ang tanan nga 441 nga publiko nga RNA-seq data set gi-mapa sa Solyntus reference genome gamit ang hisat2 (bersyon 2.1.0). Ang hybrid gene catalog nga nakuha gamit ang GeMoMa gigamit alang sa transcript-guided abundance estimation gamit ang StringTie (bersyon 2.1.1) nga adunay mga setting -t -c 5 -f 0.05 -G ug usa ka GeMoMa concatenated Solyntus1.0 gff file. Ang tanan nga naobserbahan nga ekspresyon sa usa ka 500 kb interval nga naglibot sa sli locus isip usa ka sentro gisusi, diin ang agwat sa kinatibuk-an nga 90 (inferred) gene loci nahimutang. Gikumpirma namon ang pagkawala sa bisan unsang mamatikdan nga ekspresyon sa mga sample sa SC gawas sa bisan unsang mga gene loci. Sa 500 kb interval, among gipakita ang sunod-sunod nga mas gamay nga gidaghanon sa mga kandidato nga genes sa dihang nag-intersect sa among mapping intervals I-IV nga gihubit sa ibabaw.
Confirmation sa haplotype-specific ekspresyon. Gikan sa 90 ka gipahayag nga loci sa 500 kb interval, 8 ra ang gipahayag sa ibabaw sa pinili nga threshold sa 20 FPKM sa tanang SC/SI sample. Gigamit namo kini nga mga site aron sukdon ang mga kalainan sa lebel sa ekspresyon nga haplotype-specific (Sli o sli). Ang ekspresyon nga threshold nga gipili nakapahimo sa igo nga giladmon sa pagbasa sa katapusan ug kasaligan nga bahin sa ekspresyon ngadto sa (labing daghan) nga 2 haplotypes. Kauban ang PSC locus mismo (nga walay ekspresyon sa mga tanum nga SI), kini nga 8 + 1 loci gi-haplotype sa matag usa sa 8 nga mga sample (SAMtools phase version 1.7, default settings). Ang resulta nga haplotyped (pares) nga fastq files kay de novo nga gitigom gamit ang SPAdes (bersyon 3.11.1). Ang resulta nga contigs gisala alang sa igo nga kadagaya ug gituohan nga bug-os nga gitas-on nga mRNA, nga katumbas sa nag-unang (haplotyped) nga gipahayag nga isoform. Sa pipila ka mga kaso, kini nagtangtang sa alternatibong mga spliced isoform, walay usa niini nga gisuportahan sa igo nga mga pagbasa nga adunay bisan unsang dayag nga biolohikal nga importansya. Ang pagbag-o sa kini nga mga haplotyped nga mga han-ay sa mRNA gigamit aron (dili) makumpirma kung ang usa o pareho nga mga haplotype gipahayag sa matag usa sa katugbang nga loci / sample.
Disenyo sa sli pagtukod sa ekspresyon. Gigamit namo ang han-ay sa Sli donor plant DS sa pagdesinyo sa Sli expression cassette. Aron tugotan ang lumad nga pagpahayag sa PSC, nagtukod mi og nucleic acid sequence nga naglangkob sa native promoter (1563 bp upstream sa start codon), ang tulo ka exon, ug ang native terminator (740 bp downstream sa stop codon). Busa, ang duha ka intron gikuha gikan sa PSC gene sa donor nga tanom nga DS. Kini nga han-ay gi-synthesize ug gi-clone sa pBINPLUS ni Genscript (Genscript Biotech, Leiden, Netherlands). Gipunting namon ang vector nga adunay sulud nga sli isulod isip pBINPLUS-Sli.
Pagtukod sa CRISPR-Cas9 nga vector. Gidisenyo namo ang upat ka gRNA base sa han-ay sa PGSC0003DMG400016861 sa DM4.03 sa mga lokasyon diin walay kalainan tali sa SC ug SI alleles ang anaa. Alang sa pagpili sa angay nga mga giya ug pagtukod sa vector, among gigamit ang pamaagi nga gihulagway ni Santillan Martinez et al.34. Sa mubo, upat ka sgRNA ang gipili sumala sa mga giya nga gihulagway ni Liang et al.35. Ang CC-Top CRISPR/Cas9 target prediction tool gigamit sa pagmugna og listahan sa sgRNAs36, ang pagpilo gisusi gamit ang Mfold web server37, ug ang kalihokan sa sgRNAs gitagna gamit ang sgRNA scorer38. Ang mosunod nga mga giya gipili ug gigamit sa paghimo sa vector nga pAGM: CRISPRASli: exon5.1T01 (ATTTCATCCGCGATCTCTCGGGG), exon5.1T04 (GATTTCA TCCGCGATCTCTCGGG), exon5.1T06 (TATTTCCTATTTGCTACCAGAAGG), ug exon5.1TTCTTGCCAT (TGATTCTTGAAGG), ug exon07TTCTT86966). Ang CRISPR construct dayon gi-synthesize gamit ang plasmids nga nakuha gikan sa Addgene: pICH01009 (template for amplification); pICSL0 (lebel 47751 plasmid); pICH47761, pICH47772, pICH47781, pICH47732 ug pICH1 (level 41822 plasmids); pICH4723 (linker alang sa upat ka mga giya); ug pAGM2 (level XNUMX binary vector). Ang plasmid gi-clone gamit ang E. coli Ang DH5a ug purified plasmid gipadala alang sa sequencing gamit ang mga primer PDS5843 (TTTGTGATGCTCGTCAGGGG), PDS8535 (CCCGAGAATTATGCAGCATT TT) PDS8536 (TCATCAGTCAATTACGGGGCT), ug AL717 (GCTTGGCATC AGACAAACCGGg RNA) ug pagkumpirma sa presensya sa tanan, NPTIGG.
Pagbag-o sa pBINPLUS-Sli ug ang pAGMzCRISPRASli vector ngadto sa Espesye sa tanom nga bulak ang Agrobacterium tumefaciens. Giusab namo ang pBINPLUS-Sli ngadto sa A. tumefaciens palabihan ang AGL0 ug pAGM:CRISPRASli ngadto sa A. tumefaciens strain AGL0 ug AGL1 gamit ang electroporation protocol. Nagkuha kami og 40 ka pl nga may katakus nga mga selula sa AGL0 ug gidugang ang 110 ka pl nga bugnaw nga tubig nga milliQ. Among gipipette ang 50 ka pl niini nga sagol ngadto sa precooled nga Eppendorf tubes sa yelo ug gidugang ang 1 pl sa plasmid. Gibiyaan namo ang mga selula sa yelo sulod sa 15 ka minuto ug gibalhin ang mga selula ngadto sa pre-cooled electroporation cuvettes. Gi-electroporate namo ang mga mixture gamit ang Micropulser ™ (Bio-Rad Laboratories, Vee-nendaal, Netherlands) gamit ang programa nga Ec1 (1.8 kV, 0.1 cm cuvette). Gidugang namo ang 1 ml sa LB ug gilumlom ang mga selula sulod sa 3 ka oras sa usa ka shaker sa 28 °C ug 200 RPM. Pagkahuman, among gi- inoculate ang LB agar nga mga plato nga adunay Rifampicin (100 pg/ml) ug Kanamycin (50 pg/ml) nga adunay transformation culture. Ang tanan nga gipili nga mga kolonya gikumpirma nga adunay husto nga vector.
Pagbag-o sa mga genotype sa patatas. Gibag-o namo ang genotypes B666 ug B667 nga adunay pBINPLUS-Sli ug genotypes B663 ug B665 nga adunay pAGM: CRISPRASli vector gamit ang stem explant method nga gihulagway ni Visser39. Sa mubo, ang internode explants nakuha gikan sa in vitro grown genotypes ug gibutang sa Petri dishes nga adunay R3B medium nga adunay 2 ml nga PACM medium. Ang sunod nga adlaw, 50 ml sa 48 ka oras Agrobacterium Ang mga kultura gi-centrifuged ug gisuspinde pag-usab sa 75 ml sa LB. Ang internode explants dayon gilubog sa Agrobacterium suspension sa 5 min, gipauga sa filter, ug gibutang balik sa Petri pinggan nga adunay R3B medium. Pagkahuman sa 48 ka oras nga paglumlum, ang mga explant gibalhin sa mga pinggan nga Petri nga adunay MS20 nga adunay mga antibiotics ug gibutang sa usa ka lawak sa pagtubo aron tugutan ang pagbag-o sa mga saha. Human sa pagbag-o, ang mga saha gipatubo sa MS20 media nga adunay cefotaxime (200 pg/ml), vancomycin (200 pg/ml), ug kanamycin (100 pg/ml). Kung ang mga saha nakaabot sa igo nga gitas-on, ang mga pagputol gihimo ug gipatubo sa MS20 nga wala’y antibiotics. Human sa labing menos duha ka semana nga pagtubo sa MS20 nga walay antibiotics, ang mga tanom gitanom sa greenhouse.
Pagtuki sa ploidy. Ang ploidy sa transgenic nga mga tanum ingon man ang dili nabag-o nga mga kontrol gitino gamit ang flow cytometry sa Plant Cytometry Services (Didam, Netherlands). Ang tanan nga tetraploid regenerant gilabay.
PAGE pagtuki sa CRISPR-Mga mutation nga gipahinabo sa Cas9. Ang pagkuha sa DNA, PCR, ug pagtuki sa PAGE gihimo sa Limgroup (Horst, The Netherlands). Ang mosunod nga mga primera gigamit sa pagpadako sa CRISPR-Cas9-target nga rehiyon: Forward primer: CTATTTCCTATTGCTACCAG, reverse primer: AAAACTTTACCCAAAT AACGTC. Ang pagmarka sa mga produkto sa PCR nakab-ot pinaagi sa pagdugang ug reverse primer nga adunay M13 tail (primer sequence: TGTAAAACGACGGCCAGTAAACTTTAC CCAATAACGTC) ug 700 IRDye o 800 IRDye nga may label nga M13 primer ngadto sa PCR mixture. Ang resulta nga mga produkto sa PCR gisusi sa PAGE gamit ang Li-cor system. Ang mga produkto sa PCR gikan sa kadaghanan sa mga linya nga wala’y mutation nga gipahinabo sa CRISPR-Cas9 gikuha gikan sa mga imahe sa gel aron makagama sa Fig. 3d (mga excision nga gipakita sa mga dashed nga linya).
Phylogenetic analysis sa 533 bp insertion. Ang pagkasunod-sunod sa 533 bp insertion gisusi gamit ang BLASTn sa NCBI website. Ang labing kaayo nga 30 nga mga hit, lakip ang pagsulud nga naa sa sli sa Solyntus, unya gi-download ug gi-align sa MegAlign Pro 17 (DNASTAR) gamit ang MUSCLE nga adunay default nga mga setting. Ang mga kahoy gihimo gamit ang silingan-pagdugtong nga algorithm nga adunay default nga mga setting.
Pagreport sa sumaryo. Ang dugang nga impormasyon sa disenyo sa panukiduki anaa sa Nature Research Reporting Summary nga nalambigit niini nga artikulo.
Anaa ang datos
Ang Solyntus genome sequence ug hilaw nga sequence reads anaa sa NCBI ubos sa accession PRJNA631911. Ang Solyntus genome assembly ug annotation files anaa sa WUR [https://www.plantbreeding.wur.nl/Solyntus/]. Ang RNA sequencing data gikan sa germinated pollen anaa sa NCBI short read archive ubos sa accession PRJNA713577. Ang ubang mga datos anaa sa source data file o mahimong magamit kon hangyoon. Ang tinubdan nga datos gihatag uban niini nga papel.
Nadawat: 22 Enero 2021; Gidawat: 8 Hunyo 2021;
Gipatik sa online: 06 July 2021
mga pakisayran
- 1. Duvick, DN Ang kontribusyon sa pagpasanay sa pagpatubo sa mais (Zea mays L.). Adv. Agron. 86, 83-145 (2005).
- 2. Lindhout, P. et al. Ngadto sa F1 hybrid nga binhi sa pagpasanay sa patatas. Patatas Res. 54, 301-312 (2011).
- 3. Jansky, SH ug uban pa. Pag-imbento pag-usab sa patatas isip diploid inbred line-based crop. Crop Sci. 56, 1412-1422 (2016).
- 4. Ye, M. et al. Pagmugna sa self-compatible nga diploid nga patatas pinaagi sa knockout sa S-RNase. Si Nat. Mga tanom 4, 651-654 (2018).
- 5. Enciso-Rodriguez, F. et al. Pagbuntog sa pagkadili-pagkauyon sa kaugalingon sa diploid nga patatas gamit ang CRISPR-cas9. Atubangan. Tanum nga Sci. 10, 1-12 (2019).
- 6. Su, Y. ug uban pa. Introgression sa mga gene alang sa pagsukol batok Mga infestan sa Phytophthora sa diploid nga patatas. Am. J. Patatas Res. 97, 33-42 (2020).
- 7. Dzidzienyo, DK, Bryan, GJ, Wilde, G. & Robbins, TP Allelic diversity sa S-RNase alleles sa diploid potato species. Teor. Appl. Genet. 129, 1985-2001 (2016).
- 8. McClure, B., Cruz-Garcia, F. & Romero, C. Pagkaangay ug dili pagkaangay sa S-RNase-based nga mga sistema. Si Ann. Bot. 108, 647-658 (2011).
- 9. Kubo, K. et al. Ang kolaborasyon nga dili-kaugalingon nga sistema sa pag-ila sa S-RNase nga nakabase sa kaugalingon nga dili pagkaangay. Science 330, 796-799 (2010).
- 10. De Jong, H. & Rowe, PR Inbreeding sa kultibado nga diploid patatas. Patatas Res. 14, 74-83 (1971).
- 11. Hermsen, JGT & Olsder, J. Genetics sa self-compatibility sa dihaploid sa Solanum tuberosum L. 1. Breeding kinaiya sa duha ka kaugalingon compatible dihaploids. Euphytica 25, 597-607 (1976).
- 12. Hosaka, K. & Hanneman, RE Jr. Genetics sa pagpahiuyon sa kaugalingon sa usa ka dili uyon sa kaugalingon nga ihalas nga diploid nga espisye sa patatas Solanum chacoense. 1. Detection sa usa ka S locus inhibitor (Sli) gene. Euphytica 99, 191-197 (1998).
- 13. Hosaka, K. & Hanneman, RE Jr. Genetics sa pagpahiuyon sa kaugalingon sa usa ka dili uyon sa kaugalingon nga ihalas nga diploid nga espisye sa patatas Solanum chacoense. 2. Lokalisasyon sa usa ka S locus inhibitor (Sli) gene sa patatas genome gamit ang DNA marker. Euphytica 103, 265-271 (1998).
- 14. Birhman, RK & Hosaka, K. Pagprodyus sa inbred progenies sa diploid patatas gamit ang S-locus inhibitor (Sli) gene, ug ang ilang kinaiya. Genome 502, 495-502 (2000).
- 15. Chen, J., Hu, Q., Zhang, Y., Lu, C. & Kuang, H. P-MITE: usa ka database alang sa gamay nga tanom nga balit-ad-balikbalik nga transposable nga mga elemento. Nucleic Acids Res. 42, 1176-1181 (2014).
- 16. Stefanowicz, K., Lannoo, N. & Van Damme, EJM Plant F-box nga mga protina- mga maghuhukom tali sa kinabuhi ug kamatayon. Crit. Si Rev. Plant Sci. 34, 523-552 (2015).
- 17. Liu, B., Morse, D. & Cappadocia, M. Glycosylation sa S-RNases mahimong makaimpluwensya sa pollen pagsalikway thresholds sa Solanum chacoense. J. Exp. Bot. 59, 545-552 (2008).
- 18. Laimbeer, FPE Potato genomics tulo ka paagi: quantification sa endoreduplication sa tubers, usa ka romp pinaagi sa transposon terrain, ug elucidation sa bulak kolor regulasyon. http://hdl.handle.net/10919/84480 (2018).
- 19. Clot, CR et al. Ang gigikanan ug kaylap nga panghitabo sa Sli-based selfcompatibility sa patatas. Teor. Appl. Genet. https://doi.org/10.1007/s00122-020-03627-8 (2020).
- 20. Endelman, J., Jansky, SH, Butler, N. & Christensen, G. Genetic nga ebidensya sa usa ka recessive lethal allele sa potato chromosome 12-ka-tuig nga taho sa Potato Association of America. Am. J. Patatas Res. 96, 331 (2019).
- 21. van Lieshout, N. et al. Solyntus, ang bag-o kaayo nga magkadugtong nga reference genome alang sa patatas (Solanum tuberosum). G3 Genes Genome Genet. 10, 3489-3495 (2020).
- 22. Leisner, CP et al. Genome sequence sa M6, usa ka diploid inbred clone sa high-glycoalkaloid-producing tuber-bearing potato species Solanum chacoense, nagpadayag sa nahabilin nga heterozygosity. Plant J. 1967, 562-570 (2018).
- 23. Peterson, BA ug uban pa. Self-fertility sa usa ka kultibado nga diploid nga populasyon sa patatas nga gisusi sa infinium 8303 nga patatas nga single-nucleotide polymorphism array. Genome sa tanom https://doi.org/10.3835/plantgenome2016.01.0003 (2016).
- 24. Lian, Q. et al. Pagkuha sa makadaot nga mutasyon sa panahon sa polyploidization sa patatas. Si J. Integral. Biol sa Tanum. 61, 7-11 (2019).
- 25. van Lieshout, N. et al. Solyntus, ang bag-o kaayo nga magkadugtong nga reference genome alang sa patatas (Solanum tuberosum). G3 Genes Genome Genet. 631911, g3.401550.2020 (2020).
- 26. Van Ooijen, JW JoinMap®4, Software alang sa Pagkalkula sa Genetic Linkage Maps sa Eksperimental nga Populasyon Vol. 33 (Kyazma BV, 2006).
- 27. van Ooijen, JW Katukma sa pagmapa sa quantitative trait loci sa autogamous species. Teor. Appl Genet. 84, 803-811 (1992).
- 28. Voorrips, RE Mapchart: software para sa graphical nga presentasyon sa linkage nga mga mapa ug QTLs. J. Hered. 93, 77-78 (2002).
- 29. Hirsch, CD ug uban pa. Spud DB: usa ka kapanguhaan alang sa mga han-ay sa pagmina, genotypes, ug phenotypes aron mapadali ang pagpasanay sa patatas. Genome sa tanom. 7, https://doi.org/ 10.3835/plantgenome2013.12.0042 (2014).
- 30. Bankevich, A. et al. SPAdes: usa ka bag-ong genome assembly algorithm ug ang mga aplikasyon niini sa single-cell sequencing. J. Comput. Biol. 19, 455-477 (2012).
- 31. Sharma, SK ug uban pa. Pagtukod sa reference chromosome-scale pseudomolecules alang sa patatas: paghiusa sa genome sa patatas sa genetic ug pisikal nga mga mapa. G3 Genes Genome Genet. 3, 2031-2047 (2013).
- 32. Fernandez-Pozo, N. et al. Ang Sol Genomics Network (SGN) -gikan sa genotype ngadto sa phenotype ngadto sa breeding. Nucleic Acids Res. 43, D1036-D1041 (2015).
- 33. Kim, S. et al. Ang pagkasunod-sunod sa genome sa mainit nga paminta naghatag ug mga panabut sa ebolusyon sa pungency in Capsicum mga klase. Nat. Genet. 46, 270-278 (2014).
- 34. Santillan Martinez, MI et al. CRISPR/Cas9-target mutagenesis sa tomato susceptibility gene PMR4 alang sa pagsukol batok sa powdery mildew. BMC Plant Biol. 20, 1-13 (2020).
- 35. Liang, G., Zhang, H., Lou, D. & Yu, D. Pagpili sa mga episyente kaayo nga sgRNAs alang sa CRISPR/Cas9-based nga plant genome editing. Sci. Rep. 6, 1-8 (2016).
- 36. Stemmer, M., Thumberger, T., Del Sol Keyer, M., Wittbrodt, J. & Mateo, JL CCTop: usa ka intuitive, flexible ug kasaligan nga CRISPR/Cas9 nga himan sa pagtagna sa target. NAGPUYO 10,1-11 (2015).
- 37. Zuker, M. Mfold web server alang sa nucleic acid folding ug hybridization prediction. Nucleic Acids Res. 31, 3406-3415 (2003).
- 38. Chari, R., Yeo, NC, Chavez, A. & Church, GM SgRNA Scorer 2.0: usa ka modelo nga independente sa espisye aron matagna ang kalihokan sa CRISPR/Cas9. ACS Synth. Biol. 6, 902-904 (2017).
- 39. Visser, RGF sa Manwal sa Kultura sa Tissue sa Tanum 301-309 (Springer, 1991).
Nagkabangga nga mga interes
Ang mga tigsulat wala mag-ingon nga adunay nagkasumpaki nga mga interes.
Dugang nga impormasyon
Supplementary nga impormasyon Ang online nga bersyon adunay dugang nga materyal nga magamit sa https://doi.org/10.1038/s41467-021-24267-6.
Correspondence ug ang mga hangyo alang sa mga materyales kinahanglang i-address sa CWBB
Ang kasayuran sa pagsusi sa kauban Kinaiyahan Communications salamat Roger Chetelat ug sa lain, anonymous reviewer(s) sa ilang kontribusyon sa peer review niini nga buhat. ang mga taho sa pagrepaso sa kaubanan anaa.
Impormasyon sa pag-imprinta ug pagtugot Anaa sa http://www.nature.com/reprints
Tagmantala's nota Ang Springer nga Kinaiya nagpabilin nga neutral maylabot sa jurisdictional claims sa mga na-publish nga mga mapa ug institusyonal nga mga apil.
Pasalamat
Giila namo ang tabang gikan ni Veronica Tammy Soputro sa pagbag-o sa duha ka genotype sa patatas nga adunay pAGM:CRISPRASli, ang tabang sa mga estudyante sa BSc ug MSc nga sila Gilo Pleunis, Iris Smits, Niki Vorgia, Hidde Knuiman, Maurice Geurts, Anja van Heteren, ug Torsten van der Schriek alang sa ilang tabang sa phenotyping sa mga populasyon sa pagmapa, ug Tess Lucas alang sa paghimo og mga sample sa RNA. Atong dugang nga pag-ila sa mga empleyado sa Solynta ug Wageningen University Unifarm greenhouse sa ilang tabang sa pagmentinar sa mga tanom ug pagkuha sa mga liso. Kini nga proyekto nakadawat og pinansyal nga suporta gikan sa Netherlands Organization of Scientific Research (Grant ID: NWA.17.023).
Mga kontribusyon sa awtor
Gidisenyo ug gipatuman sa E.-JE ang mga eksperimento ug gisulat ang manuskrito. Gidisenyo ug gipatuman sa AvdB ang WGS, KASP marker, ug bioinformatics nga mga pamaagi. Ang SvH, RGFV, CWBB, MEdV, ug PL nakatabang sa pagdesinyo sa pamaagi alang sa genetic mapping studies ug functional characterization sa sli. Ang RGFV, CWBB, ug PL nagrepaso ug nagkomento sa manuskrito.
ako(S) Q) Bukas nga Access Ang kini nga artikulo lisensyado sa ilalum sa usa ka Creative Commons Attribution 4.0 International License, nga nagtugot sa paggamit, pagpakigbahin, pagpahiangay, pag-apod-apod ug paghuwad sa bisan unsang medium o pormat, basta maghatag ka angay nga kredito sa orihinal nga (mga) tagsulat ug gigikanan, maghatag usa ka pag-link sa lisensya sa Creative Commons, ug ipasabut kung adunay mga pagbag-o. Ang mga imahe o ubang materyal sa ikatulo nga partido sa kini nga artikulo gilakip sa lisensya sa Creative Commons sa artikulo, gawas kung gipakita sa lain nga linya sa kredito sa materyal. Kung wala maapil ang materyal sa lisensya sa Creative Commons sa artikulo ug ang imong gitinguha nga paggamit dili gitugutan sa regulasyon sa pamatasan o molapas sa gitugotan nga paggamit, kinahanglan nga makakuha ka nga pagtugot direkta gikan sa naghupot sa copyright. Aron makita ang usa ka kopya sa kini nga lisensya, pagbisita http://creativecommons.org/ mga lisensya/ni/4.0/.









